step_nearmiss() 创建配方步骤的规范,该步骤通过根据多数类中的点与同一类中其他点的距离对点进行欠采样来删除多数类实例。
用法
step_nearmiss(
recipe,
...,
role = NA,
trained = FALSE,
column = NULL,
under_ratio = 1,
neighbors = 5,
skip = TRUE,
seed = sample.int(10^5, 1),
id = rand_id("nearmiss")
)参数
- recipe
-
一个菜谱对象。该步骤将添加到此配方的操作序列中。
- ...
-
一个或多个选择器函数用于选择使用哪个变量对数据进行采样。有关更多详细信息,请参阅
selections()。选择应产生单因子变量。对于tidy方法,当前未使用这些。 - role
-
由于没有创建新变量,因此此步骤未使用。
- trained
-
指示预处理数量是否已估计的逻辑。
- column
-
将由
...选择器(最终)填充的变量名称的字符串。 - under_ratio
-
minority-to-majority 频率比率的数值。默认值 (1) 意味着所有其他级别都会向下采样,以具有与最少出现的级别相同的频率。值为 2 意味着多数级别的行数(最多)(大约)是少数级别的行数的两倍。
- neighbors
-
一个整数。用于生成少数类新示例的最近邻居的数量。
- skip
-
一个合乎逻辑的。当
bake()烘焙食谱时是否应该跳过此步骤?虽然所有操作都是在prep()运行时烘焙的,但某些操作可能无法对新数据进行(例如处理结果变量)。使用skip = TRUE时应小心,因为它可能会影响后续操作的计算。 - seed
-
应用时将用作种子的整数。
- id
-
该步骤特有的字符串,用于标识它。
细节
该方法保留了多数类中与少数类中 k 个最近点具有最小平均距离的点。
数据中的所有列均由 juice() 和 bake() 采样并返回。
此步骤中使用的所有列都必须是数字且没有丢失数据。
在建模中使用时,用户应强烈考虑使用选项skip = TRUE,以便不在训练集之外进行额外采样。
整理
当您tidy()此步骤时,将返回包含列terms(选择的选择器或变量)的tibble。
也可以看看
nearmiss() 直接实现
under-sampling 的其他步骤:step_downsample()、step_tomek()
例子
library(recipes)
library(modeldata)
data(hpc_data)
hpc_data0 <- hpc_data %>%
select(-protocol, -day)
orig <- count(hpc_data0, class, name = "orig")
orig
#> # A tibble: 4 × 2
#> class orig
#> <fct> <int>
#> 1 VF 2211
#> 2 F 1347
#> 3 M 514
#> 4 L 259
up_rec <- recipe(class ~ ., data = hpc_data0) %>%
# Bring the majority levels down to about 1000 each
# 1000/259 is approx 3.862
step_nearmiss(class, under_ratio = 3.862) %>%
prep()
training <- up_rec %>%
bake(new_data = NULL) %>%
count(class, name = "training")
training
#> # A tibble: 4 × 2
#> class training
#> <fct> <int>
#> 1 VF 1000
#> 2 F 1000
#> 3 M 514
#> 4 L 259
# Since `skip` defaults to TRUE, baking the step has no effect
baked <- up_rec %>%
bake(new_data = hpc_data0) %>%
count(class, name = "baked")
baked
#> # A tibble: 4 × 2
#> class baked
#> <fct> <int>
#> 1 VF 2211
#> 2 F 1347
#> 3 M 514
#> 4 L 259
# Note that if the original data contained more rows than the
# target n (= ratio * majority_n), the data are left alone:
orig %>%
left_join(training, by = "class") %>%
left_join(baked, by = "class")
#> # A tibble: 4 × 4
#> class orig training baked
#> <fct> <int> <int> <int>
#> 1 VF 2211 1000 2211
#> 2 F 1347 1000 1347
#> 3 M 514 514 514
#> 4 L 259 259 259
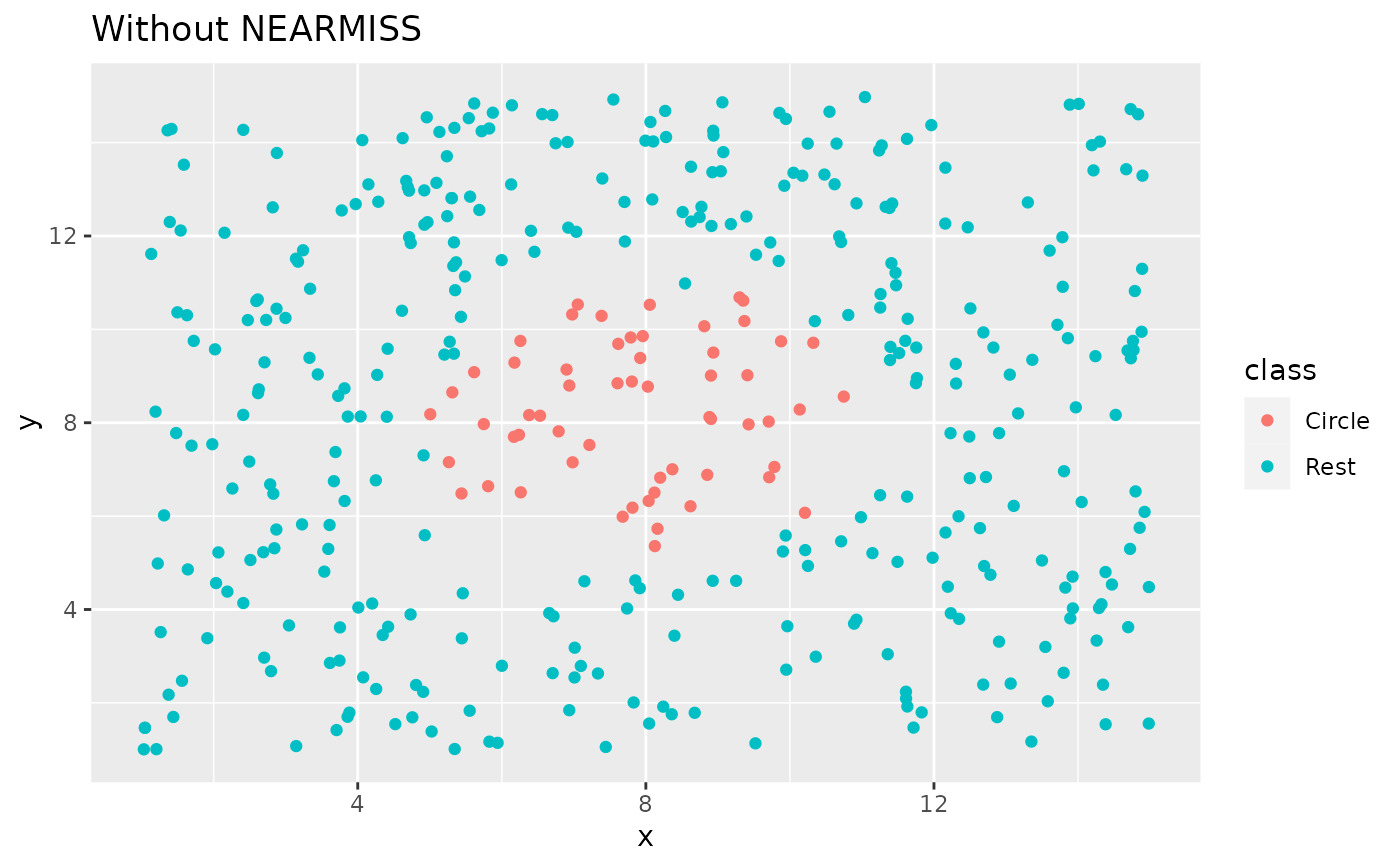
library(ggplot2)
ggplot(circle_example, aes(x, y, color = class)) +
geom_point() +
labs(title = "Without NEARMISS") +
xlim(c(1, 15)) +
ylim(c(1, 15))
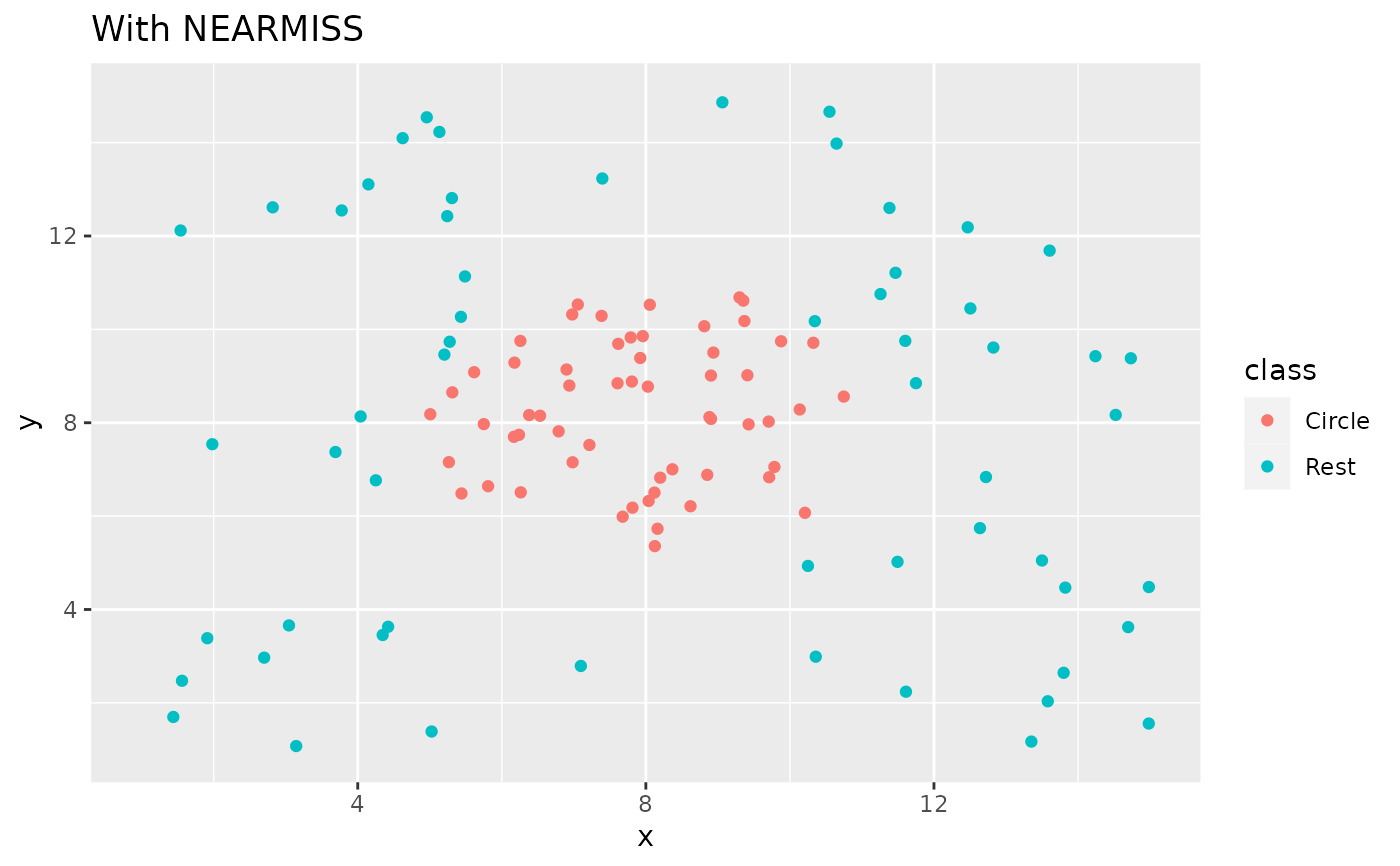
 recipe(class ~ x + y, data = circle_example) %>%
step_nearmiss(class) %>%
prep() %>%
bake(new_data = NULL) %>%
ggplot(aes(x, y, color = class)) +
geom_point() +
labs(title = "With NEARMISS") +
xlim(c(1, 15)) +
ylim(c(1, 15))
recipe(class ~ x + y, data = circle_example) %>%
step_nearmiss(class) %>%
prep() %>%
bake(new_data = NULL) %>%
ggplot(aes(x, y, color = class)) +
geom_point() +
labs(title = "With NEARMISS") +
xlim(c(1, 15)) +
ylim(c(1, 15))
相关用法
- R themis step_smote 应用SMOTE算法
- R themis step_smotenc 应用 SMOTENC 算法
- R themis step_downsample 基于因子变量对数据集进行下采样
- R themis step_tomek 删除 Tomek 的链接
- R themis step_rose 应用ROSE算法
- R themis step_upsample 基于因子变量对数据集进行上采样
- R themis step_bsmote 应用边界-SMOTE 算法
- R themis step_adasyn 应用自适应合成算法
- R themis smotenc SMOTENC算法
- R themis smote SMOTE算法
- R themis tomek 删除 Tomek 的链接
- R themis bsmote 边界-SMOTE算法
- R themis nearmiss 删除其他类附近的点
- R themis adasyn 自适应合成算法
- R update_PACKAGES 更新现有的 PACKAGES 文件
- R textrecipes tokenlist 创建令牌对象
- R print.via.format 打印实用程序
- R tibble tibble 构建 DataFrame 架
- R tidyr separate_rows 将折叠的列分成多行
- R textrecipes step_lemma 标记变量的词形还原
- R textrecipes show_tokens 显示配方的令牌输出
- R tidyr extract 使用正则表达式组将字符列提取为多列
- R prepare_Rd 准备用于渲染的解析 Rd 对象
- R tidyr chop 砍伐和砍伐
- R tidyr pivot_longer_spec 使用规范将数据从宽转为长
注:本文由纯净天空筛选整理自等大神的英文原创作品 Remove Points Near Other Classes。非经特殊声明,原始代码版权归原作者所有,本译文未经允许或授权,请勿转载或复制。
